R语言读取和修改 fcs文件
记住要从上往下一个一个包的安装,已经安装了的就不用安装,如果就是 读取和修改fcs文件,只需要安装 flowCore包就可以了。
if (!requireNamespace("BiocManager", quietly = TRUE))
install.packages("BiocManager") ##数据源:
BiocManager::install("flowWorkspaceData") ##数据读取和质控:
BiocManager::install("flowCore")BiocManager::install("flowClean") ##批量标准化:
BiocManager::install("flowStats") ##自动圈门包:
BiocManager::install("openCyto")BiocManager::install("flowDensity") ##结果的可视化:
BiocManager::install("ggcyto")BiocManager::install("flowViz")
读取FCS文件的方法:
这个代码已经验证可以使用:
library(flowCore) library(ggcyto) data <- read.FCS("fcs/Hep5.fcs", transformation=FALSE) data1 <- exprs(data[,])##获取对应的信号的值 data1 write.csv(data1,"fcs/Hep5_04.csv",row.names = FALSE)
上述代码中data的结构图如下:
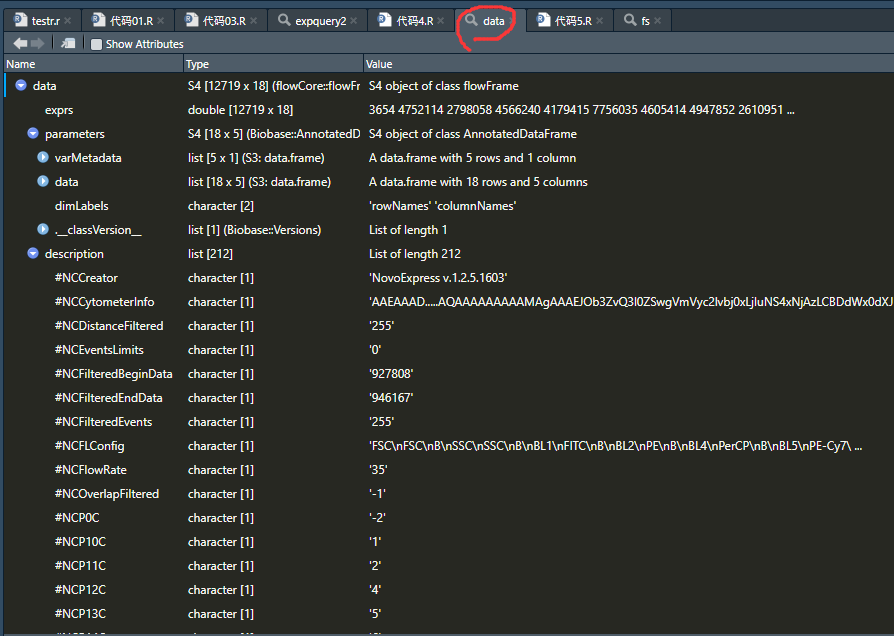
构建 flowFrame的代码:
new("flowFrame", exprs = ...., Object of class matrix parameters = ...., Object of class AnnotatedDataFrame description = ...., Object of class list )
这个方法也可以实现:
library(flowCore)
fs <- read.flowSet("fcs/PANC-1-7.fcs")
fs
sampleNames(fs)
#data1 <- exprs(fs[[1]][1:12,])##获取数据
data1 <- exprs(fs[[1]][,])##获取数据
data1
write.csv(data1,"fcs/PANC-1-7_05.csv",row.names = FALSE)
上面代码中 fs的结构如图:
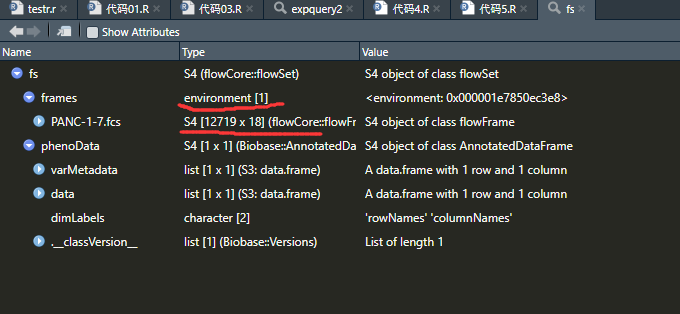
在R语言中,环境(environment)是一个存储变量和函数的地方,可以看作是存储对象的容器。每个环境都有一个父环境,形成一个环境链。在R中,函数中定义的变量和函数都存在于函数的环境中。
修改FCS文件的数据方法:
参考:https://cloud.tencent.com.cn/developer/article/1756347
library(flowCore) library(ggcyto) data <- read.FCS("fcs/Hep5.fcs", transformation=FALSE) data@exprs[1,1] <- 3654 #举例修改其中的一个值,如果是从excel中读取值来进行修改,那就用 apply函数族实现赋值修改 write.FCS(data,"Hep_01.fcs") #生成新的 FCS文件

